森基金成果報告書
解法混在非同期型細胞シミュレーションシステムの開発
博士課程2年 高橋恒一
概要
本研究では全細胞規模での精密なシミュレーションを可能にするための理論
的、技術的基盤を整備、開発している。具体的には、まず細胞オブジェクト
モデリング理論、シミュレーションアルゴリズムおよび解析手法の開発を行
う。次にこれらの理論基盤の開発と並行して細胞シミュレーションのための
ソフトウエアプラットフォームであるE-CELL Simulation Environmentを継続
的に開発、改良する。さらに大規模なモデリング/シミュレーションのための
プロジェクト管理手法やツール群を開発を行う。本年度は特にE-CELL
Simulation Environmentの次世代版であるE-CELL 3の開発に力を入れた。
成果
別々のスケジューリングポリシーで自律的に計算を行う多数の計算モジュー
ル間のスケジューリングアルゴリズムを動的優先順位付きキューを基本として
完成、実装
モデリング/シミュレーションのためのクラスライブラリ(libecs)、
libecsにAPIを提供するfacadeであるlibemc、libemcのpython言語bindingであ
るpyecsの三層構造のアプリケーションフレームワークの実装を完了
python言語によるフロントエンド記述のためのアプリケーション
フレームワークおよびセッションフレームワークを設計、実装。共同研究者達により
GUIセッションモニター、数理解析モジュールなどの実装が開始。
複数の生物学データベースから半自動的にモデルを生成し、モデラーに
よるモデリングを支援し、シミュレーション、数理解析までを統一的に支援す
るモデリング環境を設計
発表実績等
[2001年5月] 日本人工知能学会(島根)で発表
[2001年5月中] E-CELL 3開発者向けアルファ版リリース
[2001年6月初旬] カリフォルニア工科大で開発中の細胞モデル言語SBML の次
期版の仕様策定会議参加のため渡米
[2001年7月] Objects in Bio/Chem-informatics 01
(デンバー)で発表
[2001年8,9月] 先端生命科学研究所(鶴岡)に滞在、集中開発期間
[2001年9月28日] E-CELL 3.0 alpha 1リリース (開発者向け)
[2001年12月] Genome Informatics Workshop(東京)、日本分子生物学会で一般発表
[2001年12月] IEEE
Intelligent Systems誌に論文投稿
[2002年2月1日] E-CELL 3.0 alpha 2リリース (開発者向け)
[2002年4月2日] E-CELL 3.0 beta 1リリース予定
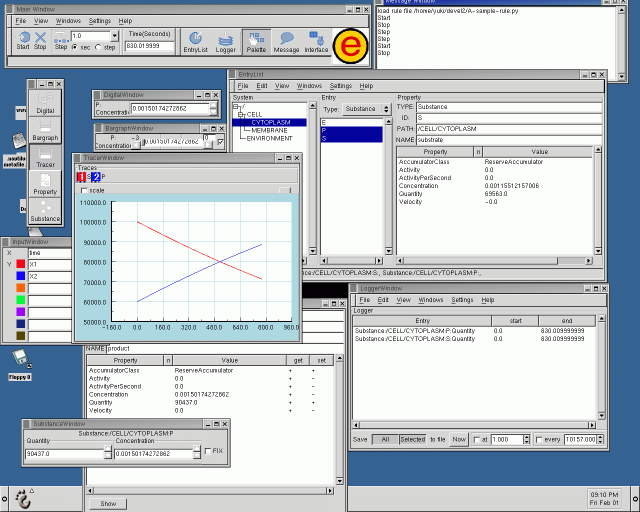
下図:E-CELL 3上に構築されたOsogo GUI セッションモニタのスクリーンショット
 <>
<>
Resources
e-cell.org
E-CELL 3開発プロジェクトサマリ (bioinformatics.org)
E-CELL Simulation Environment HQ
 <>
<>
 <>
<>